ProteoformX™是一款功能强大且用户友好的软件平台,采用MAM策略,在proteoform层面对生物药产品进行表征分析。ProteoformX提供了集成的分析工作流程,能够支持从蛋白质组学研究到生物药分析等各种proteoform层面的分析任务。通过高效的完整分子量分析,全局评估可检测到的多变的蛋白质变体(proteoforms),同时结合Top-Down分析,实现蛋白质完整序列匹配、精准翻译后修饰位点定位及定量分析。
软件搭载全新设计的New Peak Detection和Peptide Mapping两大功能模块,以更高的准确率、更快的分析效率和结果置信度,为 proteoform 研究提供更深入的解析视角。软件符合CFR法规要求,可在各类临床及生物制药应用场景中保障数据完整性与安全性,并满足合规审计的要求。
Key Features
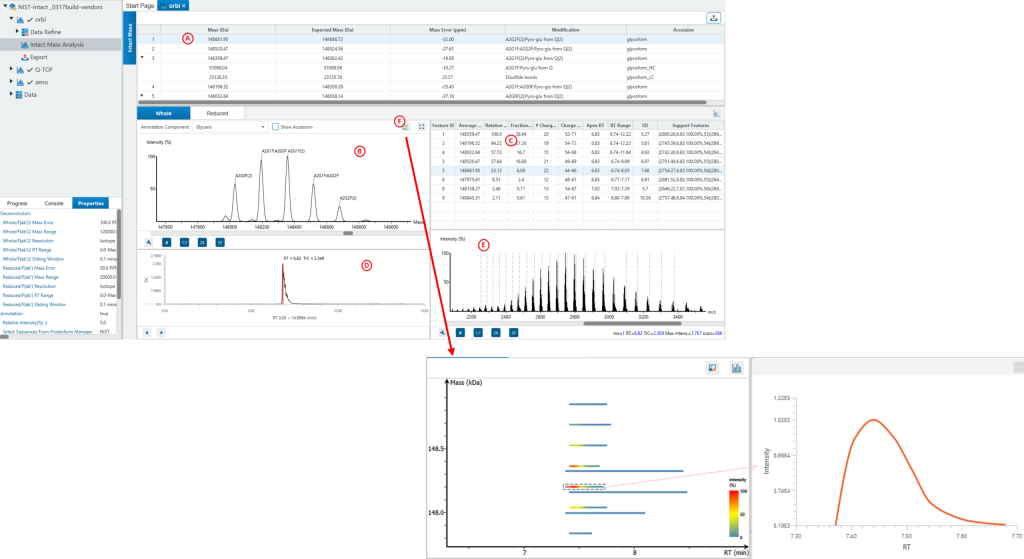
 Intact Mass 分析
Intact Mass 分析
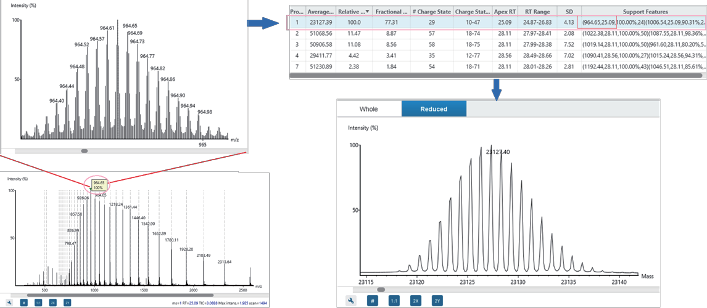
高精度质谱解卷积
基于特征峰的质量解卷积算法能够以高灵敏度和特异性识别proteoform的质量,适用于同位素区分的高分辨和低分辨的数据,可处理广泛的样本类型。
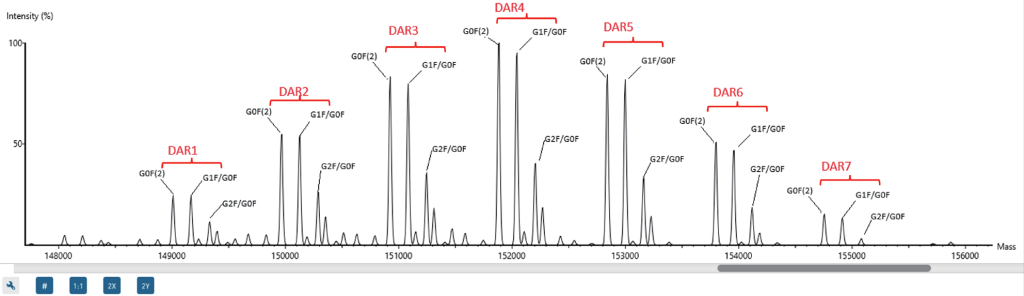
翻译后修饰和ADC药物载荷的全面注释
Intact Mass分析模块可为proteoform复合体和亚基提供准确注释,即使是带有修饰和ADC药物载荷的高度异质性的样本也适用。
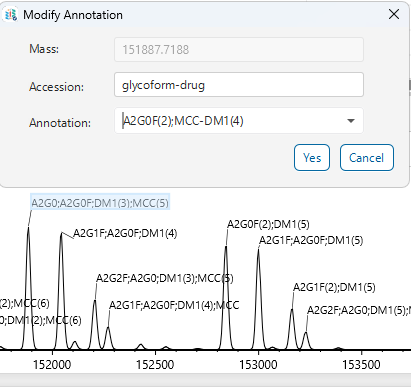
支持结果的人工校验与注释
默认情况下,软件会按照理论值与实测值之间质量误差最小的原则完成注释分配。但该结果并非总能契合预期,也不一定具备对应的生物学关联意义。借助新增的人工注释功能,用户可依托自身专业知识手动筛选备选匹配条目,也可直接输入自定义注释内容。
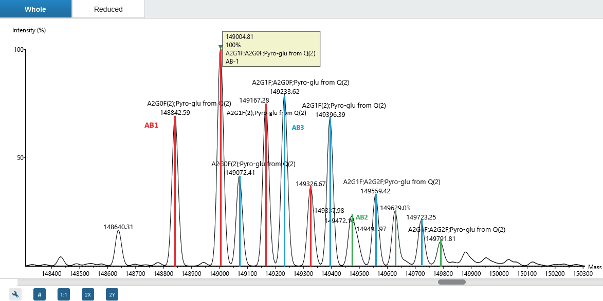
蛋白质水平上的糖基化分析
完整分子量解卷积技术可精确检测抗体混合物中的糖基化proteoforms。
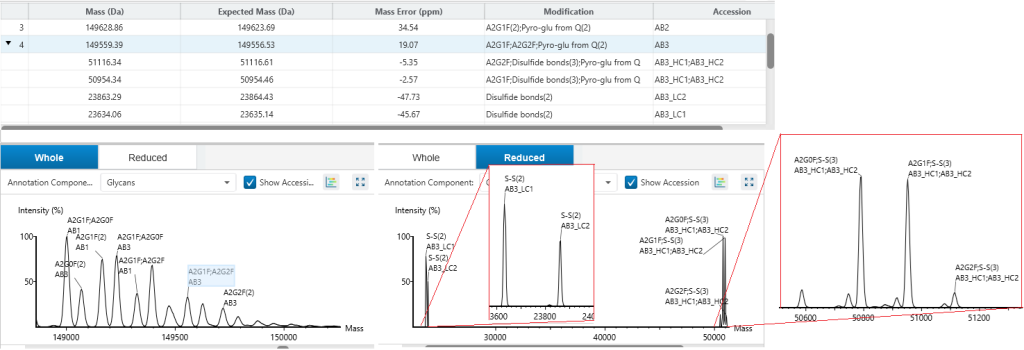
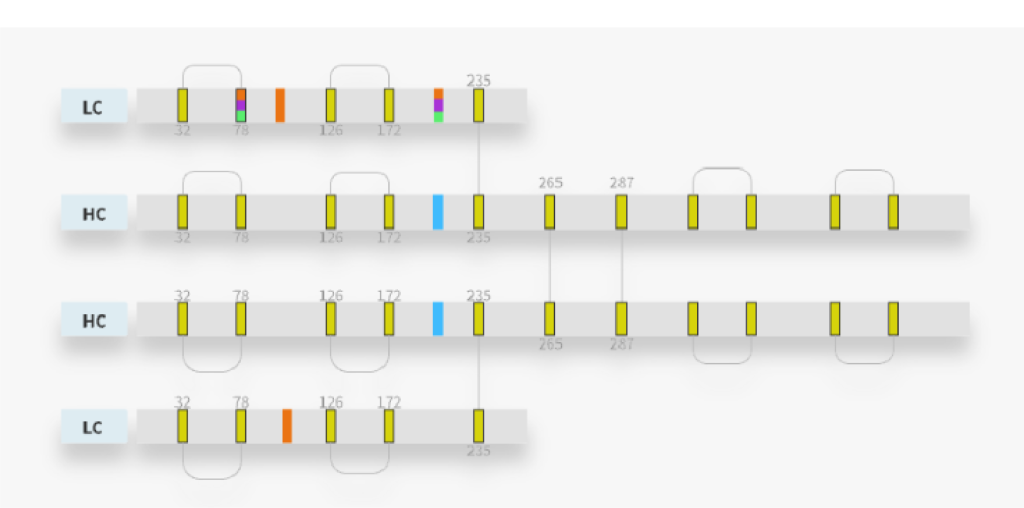
抗体重链与轻链配对分析
完整分子量蛋白质注释可确定抗体重链与轻链的配对方式,从而对所有抗体形式(包括不对称抗体和混合物)进行全面表征。
全面的结果可视化
ProteoformX™ 提供全面的分析结果,包括带有注释峰的交互式谱图视图以便用于透明化解析,以及解卷积得到的所有质量数表格中 support feature 信息,可直接用于指导靶向top-down的MS/MS实验。
 Top-down蛋白质组搜索
Top-down蛋白质组搜索
Top-down质谱技术可实现Proteoform的表征,包括精确的翻译后修饰定位。然而,数据复杂性和序列覆盖度有限等挑战可能会限制分析和通量。在ProteoformX™中,其用户界面可帮助用户对从原始数据到鉴定结果的全流程进行手动核查。ProteoformX支持多种碎裂方法(CID、HCD、ETD、ETHCD,UVPD)。
![]() Bottom-up辅助的Top-down/middle-down质谱分析
Bottom-up辅助的Top-down/middle-down质谱分析
![]() 通过分层级追踪每一种proteoform
通过分层级追踪每一种proteoform
![]() 支持多种碎裂方法
支持多种碎裂方法
![]() 开放搜索
开放搜索

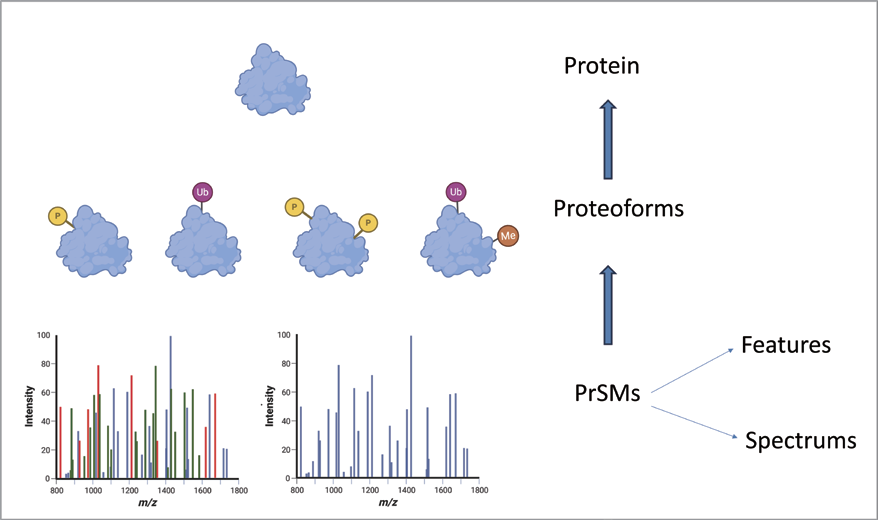
ProteoformX™ 软件通过基于特征峰的鉴定算法,提供层级化展示信息。
具有灵活的用户交互界面,可实现不同视图之间的链接,从而能够让用户无缝获取从原始数据到蛋白质形态谱匹配(PrSM)及蛋白质推断的信息。
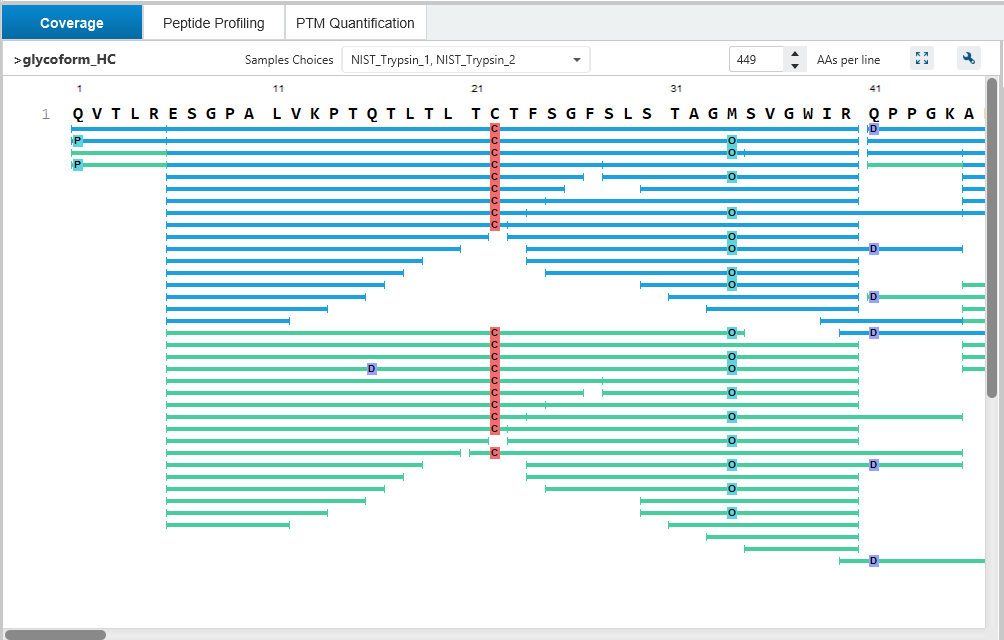
在Protein tab中,Coverage视图展示了映射至蛋白质序列上的不同的proteoforms,而Peptide coverage视图则显示所有来自bottom-up质谱分析所匹配到该蛋白质序列的所有肽段。在Coverage视图中灰色条带代表已匹配至蛋白质序列的区域具有质量偏移或者有翻译后修饰的片段,但未找到碎片离子用于准确定位。
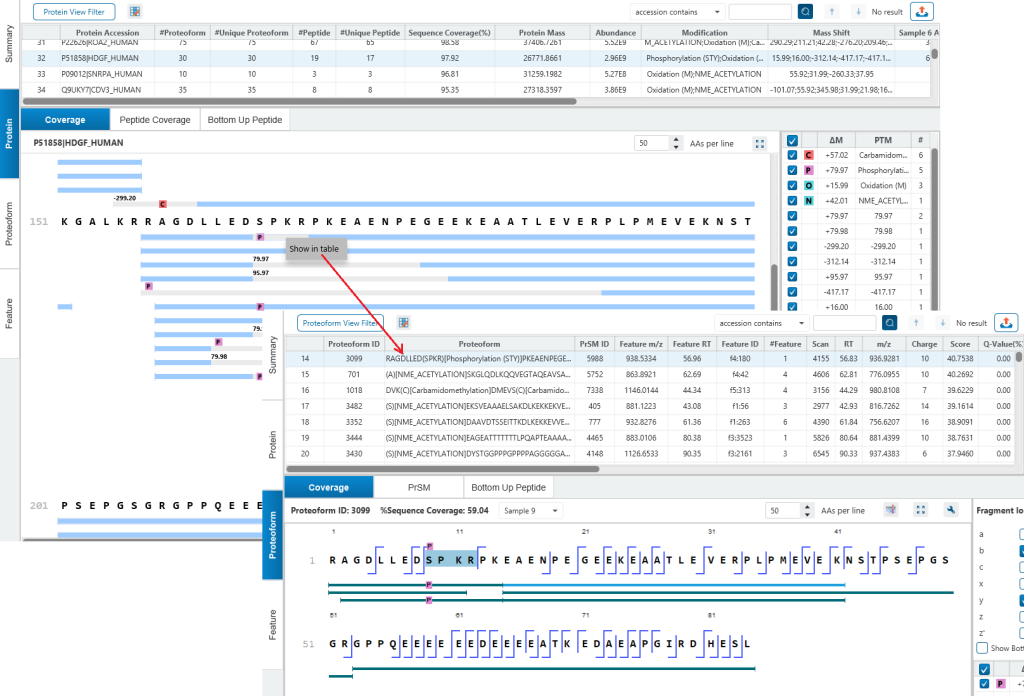
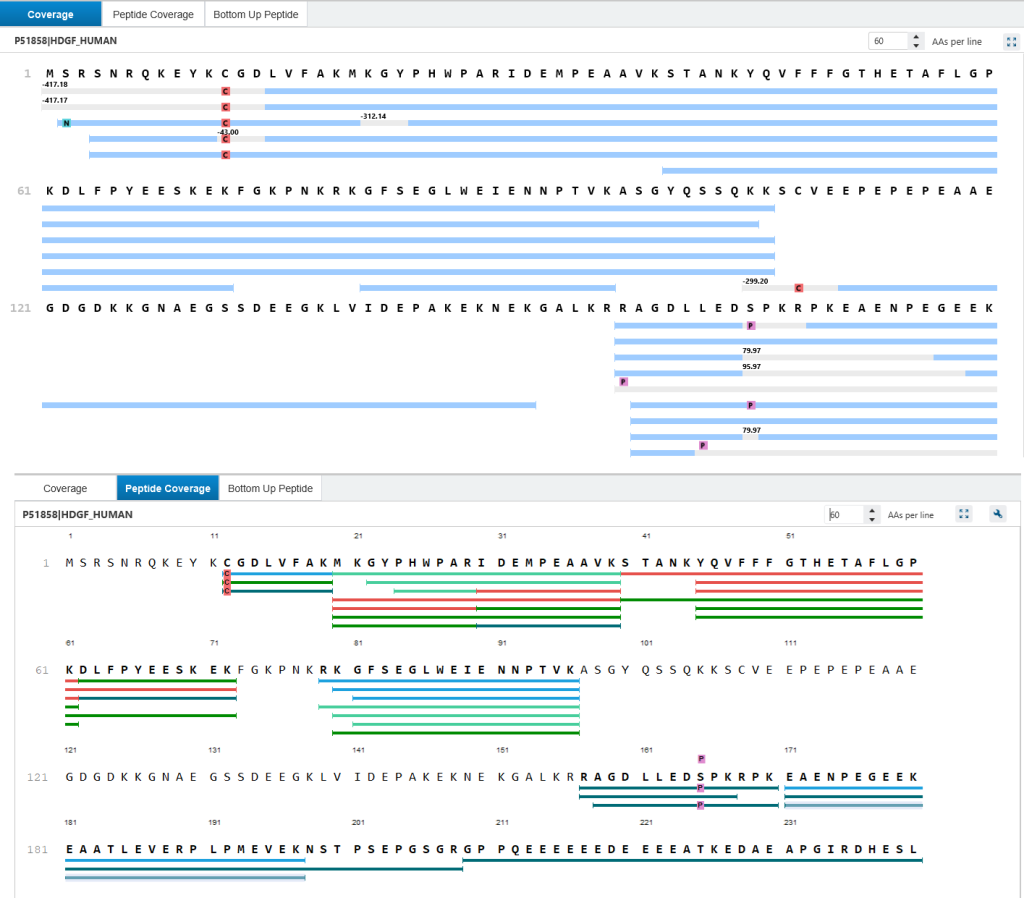
在 Proteoform tab中, 序列覆盖度由top-down碎片离子支持的氨基酸序列百分比来定义。相对于氨基酸序列质量的修饰或是质量偏移会在结果视图中呈现。若某修饰可通过bottom-up数据定位到单个氨基酸,top-down碎片中对应的残基将标黄突出显示。
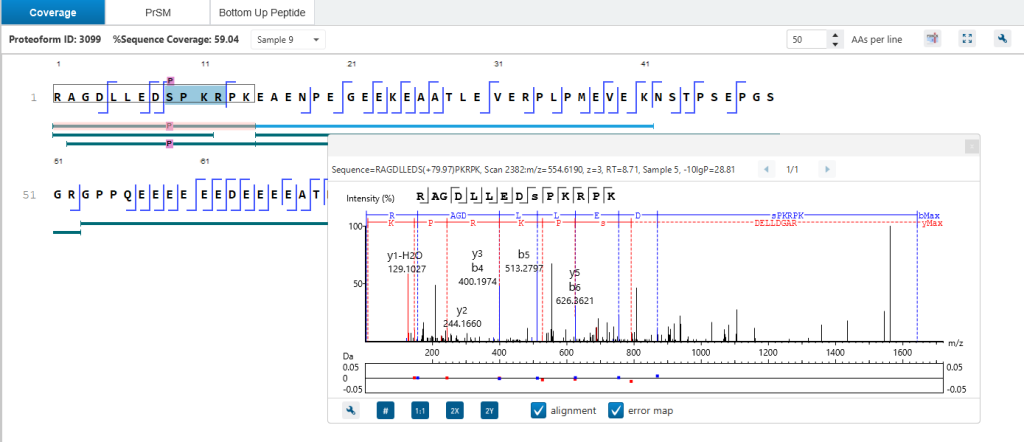
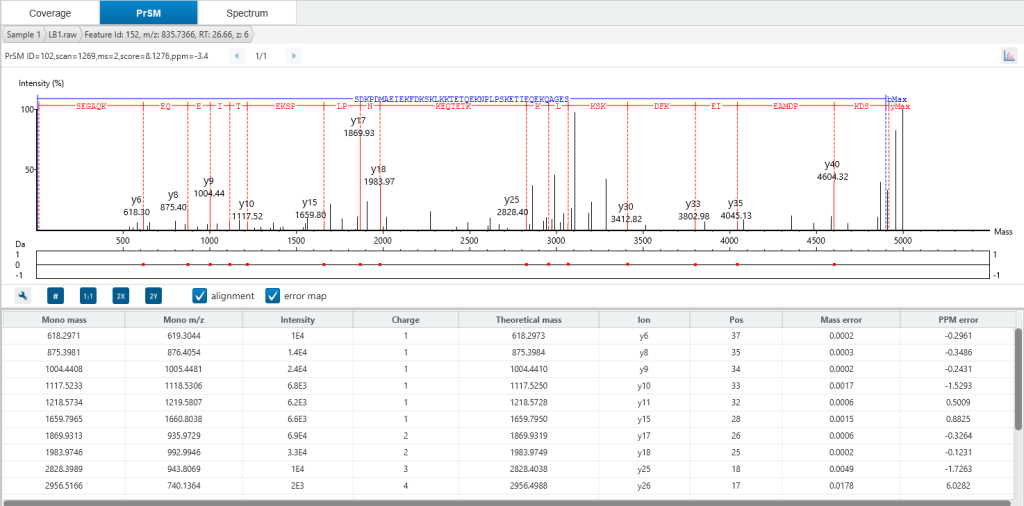
深入查看 Proteoform tab,可以看到每个proteoform鉴定结果是如何以高质量PrSMs(Proteoform Spectrummatch)、碎片离子质量表和交互式序列碎裂图作为支撑的。ProteoformX™的“Spectrum tab”将理论母离子峰和碎片离子分别直接叠加到MS1和MS2谱图上,可直观看到同位素峰簇分布,评估离子隔离窗口,精准定位参与解卷积的离子,获取哪些谱是来自嵌合谱图的信息。不同颜色和形状注释清晰区分离子类型、匹配与未匹配碎片,为结果提供透明度与可信度。
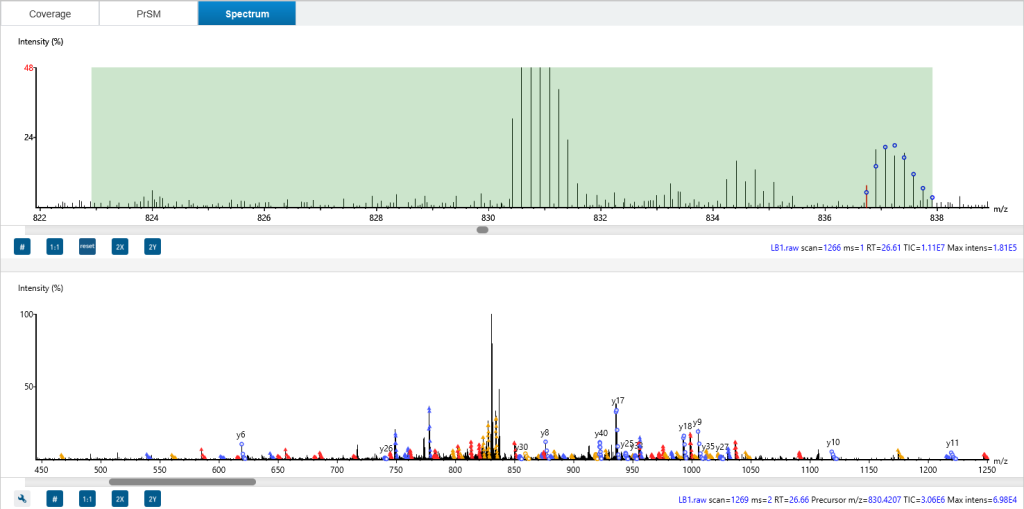
基于特征峰的LC-MS视图
基于特征峰算法,ProteoformX™ 提供包含ms/ms谱图及其相关MS1特征峰的LC-MS视图。可放大以详细查看每个特征峰。
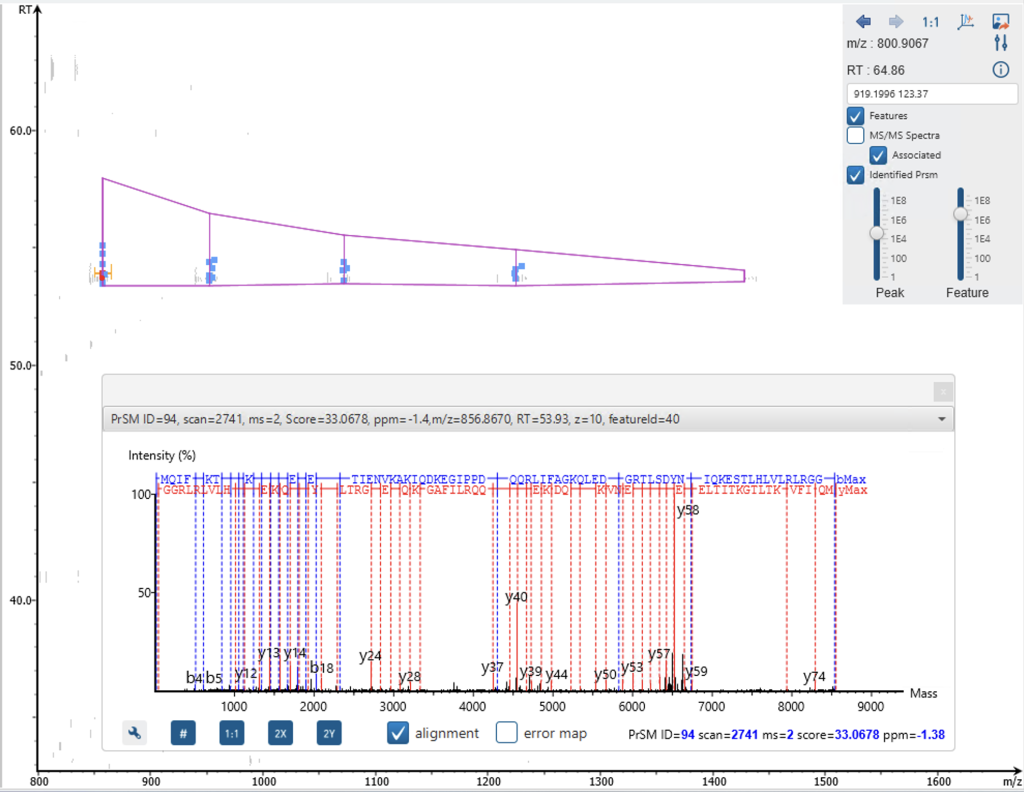
深入的Top-down蛋白质组鉴定与开放搜索(open search)
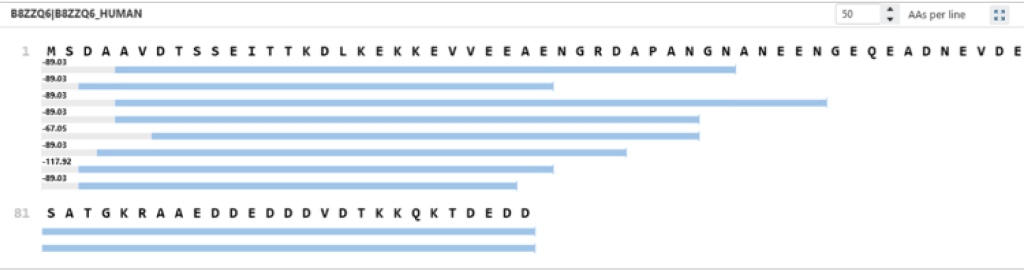
通过启用OpenPTM搜索功能,允许检测预期以外的修饰和蛋白质的截断形式,从而提升Proteoform的鉴定能力。在以下示例中,未启用OpenPTM搜索时仅鉴定出B8ZZQ6蛋白的2种C端Proteoform,而启用后可检测到8种。其中新增的一种Proteoform呈现‒89.03 Da的质量偏移,这与N端蛋氨酸缺失伴随乙酰化修饰(一种常在Protein N端被观察到的修饰)的特征一致。通过扩展搜索空间以包含质量偏移和非规范末端[non-canonical termini],OpenPTM搜索可实现更全面的Proteoform分析。

 New Peak Detection
New Peak Detection
New Peak Detection 可识别新增特征峰,并对生物药物代谢产物、产品相关杂质及分子水平的变化进行追踪监测。是利用质谱技术对复杂生物药物分子进行表征的核心工具,可对含非天然氨基酸、核苷酸的肽段,以及支链肽和环肽进行分析,并可通过人工校验完美适配药物研发工作流。
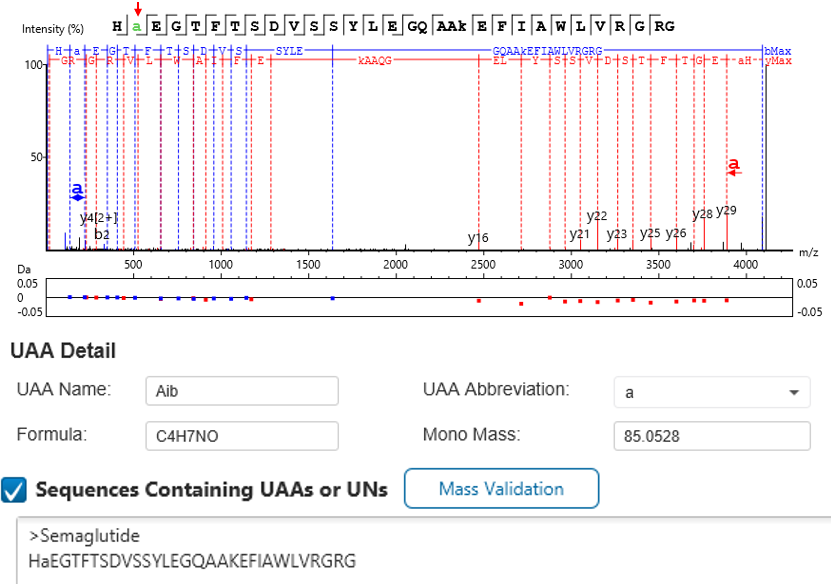
含非天然氨基酸与核苷酸肽段的表征分析
多肽类治疗药物通常含有非天然氨基酸(UAA)与非天然核苷酸(UN)。而常规质谱数据分析工具存在局限,仅支持对标准氨基酸进行检索分析。
在New Peak Detection中用户可以自定义非天然氨基酸 / 非天然核苷酸,结合 MS1 与 MS2 数据,实现可靠的定性和定量,并对分子变化趋势进行监测,从而提升对复杂多肽类生物药的精准分析与表征水平。

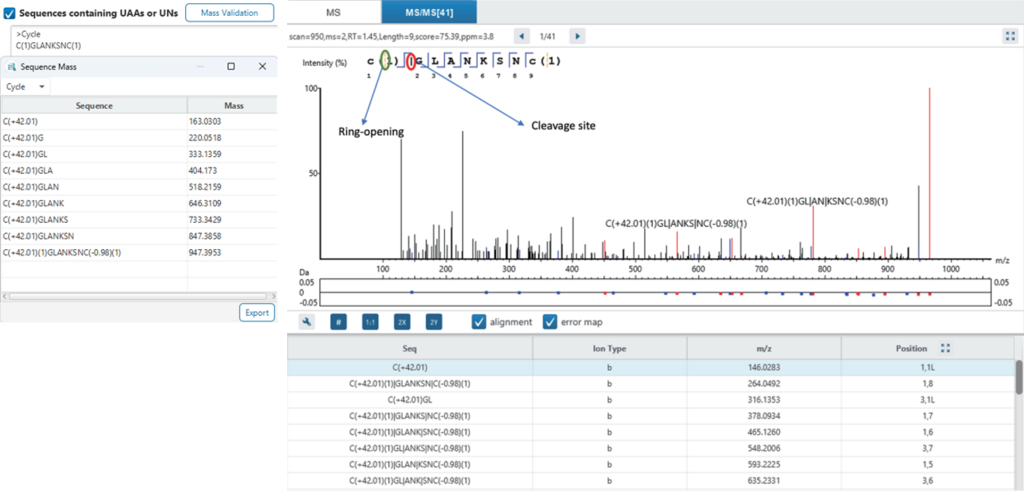
线性肽、支链肽与环肽的表征分析
多肽类生物药一般并不是简单的线性分子,其结构可包含支链或环状等复杂结构,因此需要针对性的注释与分析方法。
New Peak Detection 支持线性、支链及环状结构分析,可为支链位点、开环位点及环肽裂解碎片提供专属的MS2注释(黄色虚线表示二硫键处发生开环,黑色竖线为裂解位点)。
此外,为帮助用户验证输入信息的准确性,软件提供质量验证工具,可计算不同裂解位点所产生的理论质量,从而实现对复杂分子变异趋势的高灵敏度监测。可基于背景蛋白 FASTA 数据库进行杂质匹配定位,或通过从头测序方法鉴定新肽段。

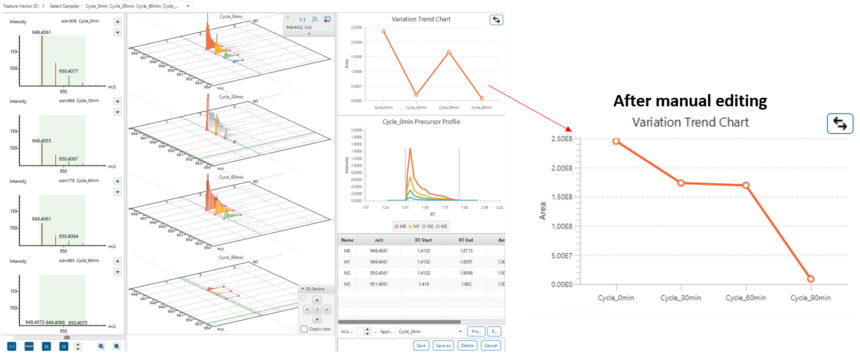
特征峰的手动编辑
自动特征峰检测可能因降解产物浓度偏低、峰形拟合偏差或基质效应等因素,遗漏部分特征峰信号。特征峰编辑功能专为解决此类问题而设计,支持用户在目标谱图中,对检测有误或此前未被识别的特征峰进行手动精准选取与定义。点击特征峰编辑按钮,即可进入手动调整特征峰的操作界面。
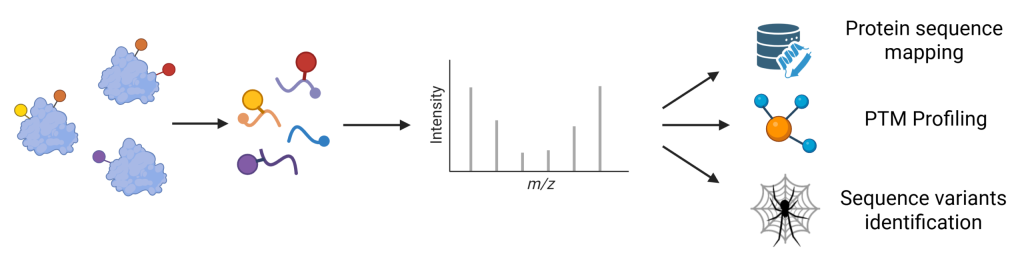
 Peptide Mapping
Peptide Mapping
Peptide Mapping是ProteoformX最新推出的特色工作流之一。 该流程可对酶解样品中的proteoform进行表征分析,包括将肽段序列匹配至各类proteoform,并基于肽段水平信息完成翻译后修饰(PTM)与序列变体的鉴定。

借助翻译后修饰(PTM)表征功能,bottom-up 质谱数据现已可用于解析目标蛋白质的完整 proteoform 全貌。
依托PEAKS PTM与openPTM检索算法,Peptide Mapping不仅可实现已知及常见修饰的定性和定量,还能识别非常见与未知修饰。结合序列变体分析功能可进行突变位点鉴定,此模块可帮助用户全面获取潜在proteoform信息,为功能机制研究提供依据。
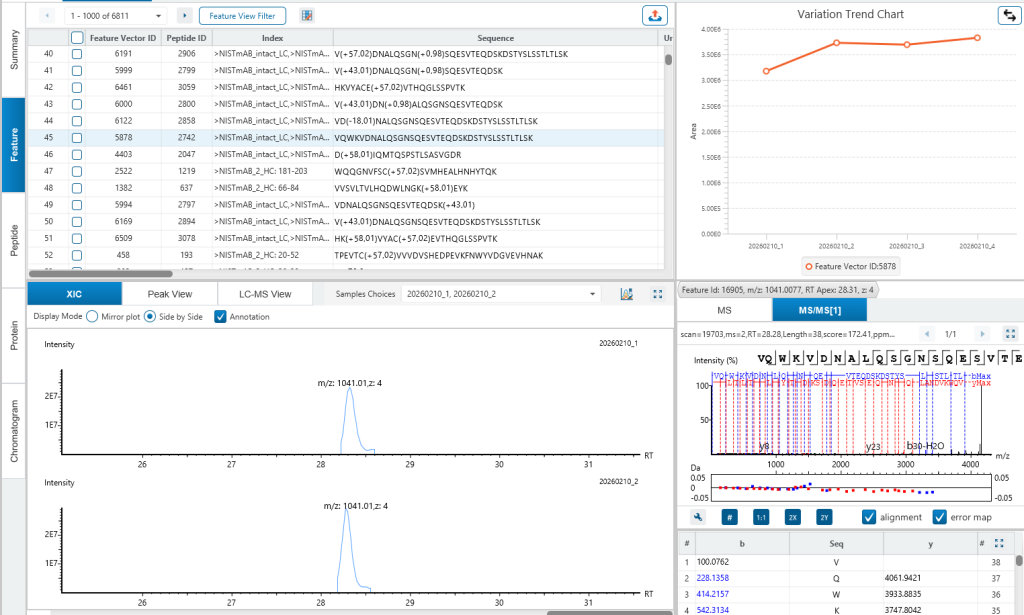
除优化升级的定性分析功能外,用户还可对样品间的定量差异进行分析。在Feature或Peptide列表中选取代表性肽段,即可手动考察不同样品间肽段丰度的变化情况,为功能表型分析或批次差异判定提供依据。
 Proteoform Manager
Proteoform Manager
灵活定义和可视化Proteoform变体
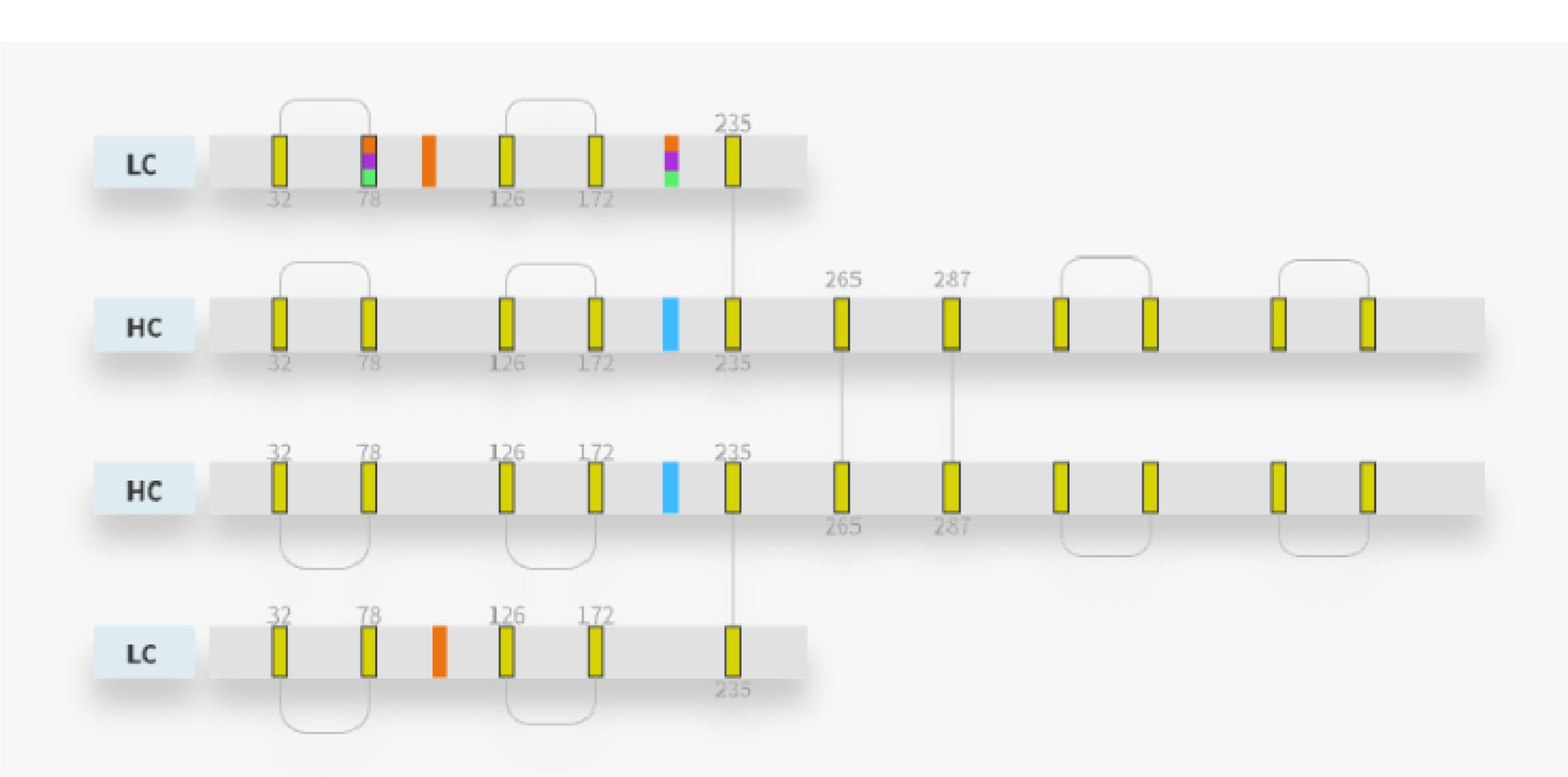
ProteoformX™ 中的 Proteoform Manager 提供了直观的界面,可用于定义链内与链间连接、切割位点、位点特异性翻译后修饰(PTM)以及糖基化。这些功能支持对生物制药分析相关的复杂proteoform进行全面建模。
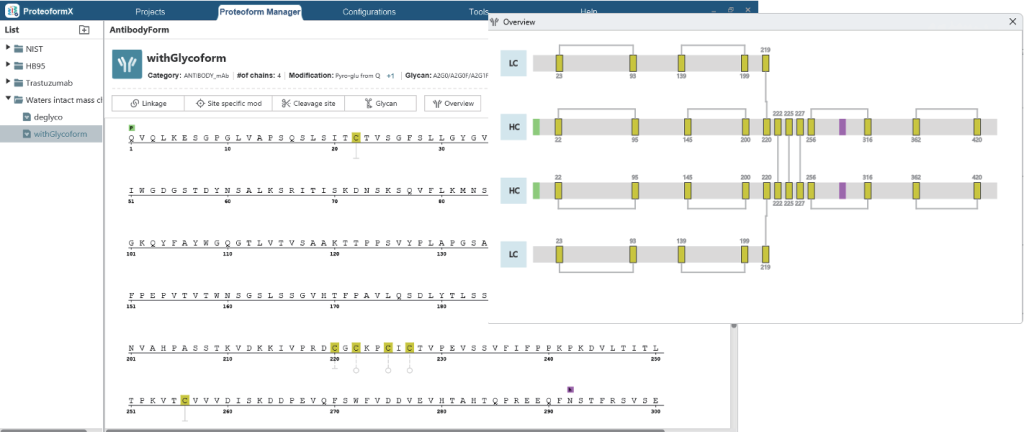
例如,轻松使用的Proteoform Manager在Proteoform水平定义抗体,包括位点特异性修饰、糖基化形式、连接和切割位点。
References & Resources
Li K, Shan B, Xin L, Li M, Wang L. Proteoform search from protein database with top-down mass spectra. Nat Comput Sci. 2025 Nov;5(11):998-1009. doi: 10.1038/s43588-025-00880-z. Epub 2025 Oct 3. PMID: 41044386.
Basharat AR, Zang Y, Sun L, Liu X. TopFD: A Proteoform Feature Detection Tool for Top-Down Proteomics. Anal Chem. 2023 May 30;95(21):8189-8196. doi: 10.1021/acs.analchem.2c05244. Epub 2023 May 17. PMID: 37196155; PMCID: PMC10233584.
Choi IK, Liu X. Top-Down Mass Spectrometry Data Analysis Using TopPIC Suite. Methods Mol Biol. 2022;2500:83-103. doi: 10.1007/978-1-0716-2325-1_8. PMID: 35657589.
Roberts, D.S., Loo, J.A., Tsybin, Y.O. et al. Top-down proteomics. Nat Rev Methods Primers 4, 38 (2024). doi:10.1038/s43586-024-00318-2
Evaluating critical quality attributes of bispecific antibodies by multi-level mass spectrometry