基于服务器的高通量多用户符合CFR标准的发现型蛋白质组学LC-MS/MS分析软件
借助 PEAKS Online 13 的强大计算资源,可支持多用户同时开展LC-MS/MS蛋白质与肽段的鉴定及定量分析。重构后的平台具备更高的大型数据集处理效率,可灵活部署于任意多 CPU 服务器、本地集群或云端,此外新版本符合CFR法规要求,全面保障数据完整性、安全性,并满足监管审计的前置筹备要求!全面支持DDA与DIA,PEAKS Online 13 为您提供强大而完备的解决方案,助力您的研究迈向新高度!

联系我们获取PEAKS Online 13 !
核心功能
高性能计算的分布式系统
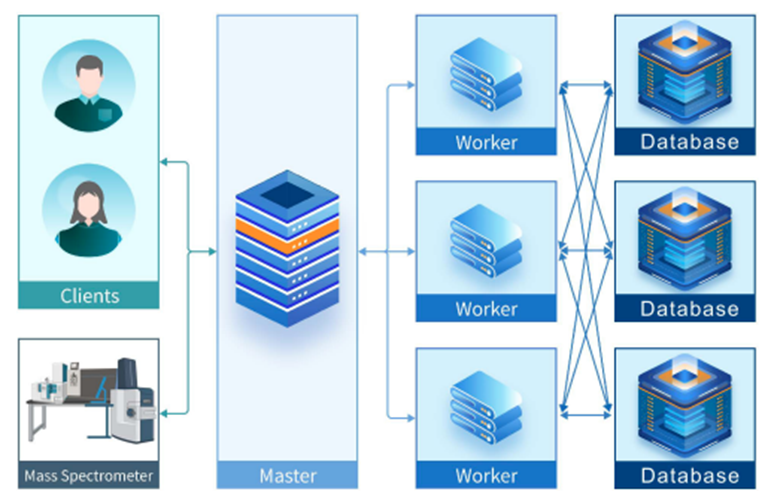
PEAKS Online 采用最新分布式计算技术,为网络中的多用户提供高通量运算性能,支持同时运行PEAKS工作流。系统以主节点为核心,负责接收来自客户端的计算请求,并将计算任务分配给工作节点。工作节点执行实际的数据处理与计算任务,确保系统高效运行。
高通量与扩展性
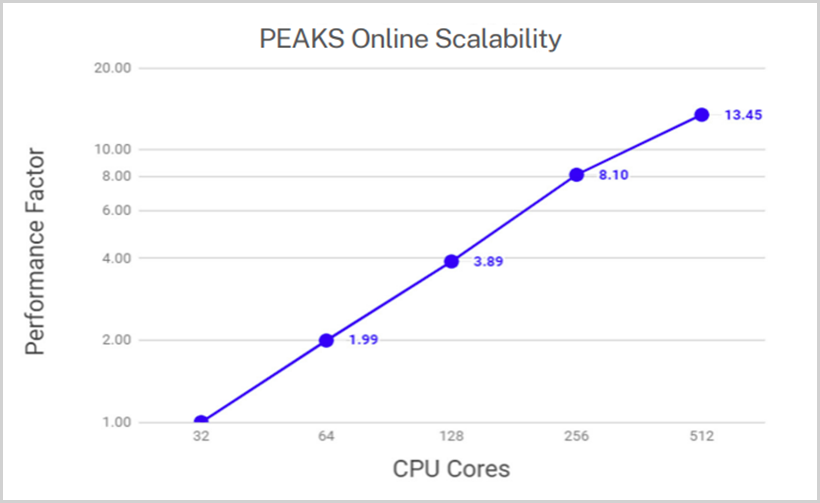
PEAKS Online 是一款专为大规模项目与多用户场景设计的蛋白质组学数据分析平台,支持项目级与数据级的并行处理。通过灵活添加工作节点与数据库节点,系统可实现垂直扩展(提升单节点性能)和水平扩展(增加节点数量),从而满足不断增长的计算需求。
双界面设计
PEAKS Online 提供双界面设计,确保轻松集成到任何蛋白质组学工作流程中。其中 Web 客户端界面支持用户通过可视化方式设置与提交项目,并查看验证分析结果;而客户端命令行界面(CLI)则可集成到现有分析流程中,实现完全自动化的数据处理。

网页客户端界面
访问管理工具
创建、查看及共享项目
监控运行进程并调整优先级
全平台兼容
随时随地通过任何电脑轻松创建和访问PEAKS项目。使用 PEAKS Online,用户无需安装任何软件即可访问服务器 ,只需打开网页浏览器(如谷歌浏览器 Chrome、微软 Edge),即可设置 PEAKS 数据库搜索任务并查看分析结果。当您的搜索任务完成后,系统还会自动发送邮件通知您任务已完成。

客户端命令行界面
自动化批量数据处理
定义标准化工作流程
轻松集成至现有分析流程
减少人工干预
命令行界面(CLI)支持用户实现全自动化的数据分析。只需创建标准化工作流,当数据生成并存入存储库后,PEAKS Online。通过客户端 CLI 生成的结果可自动导出为 .csv 文件,或通过 PEAKS Online Web 客户端进行查看。
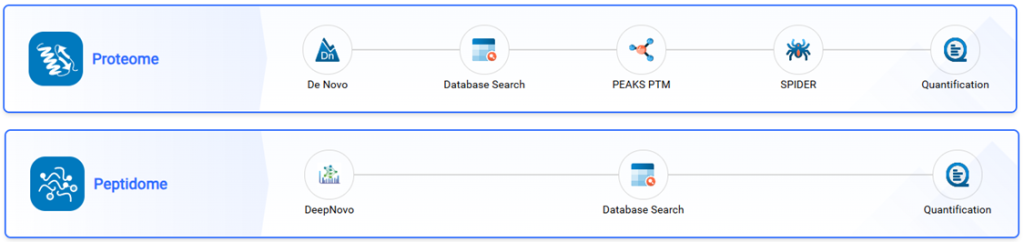
蛋白质组和多肽组驱动的工作流
在 PEAKS Online13 中,数据依赖型采集(DDA)与数据非依赖型采集(DIA)工作流已精简为两种核心选择:蛋白质组分析和多肽组分析。用户可通过选择运行或修改特定步骤,定制专属分析工作流。分析结果将按直观的结果节点分类呈现,让您更轻松地解读、探索和验证数据。
DDA
DIA
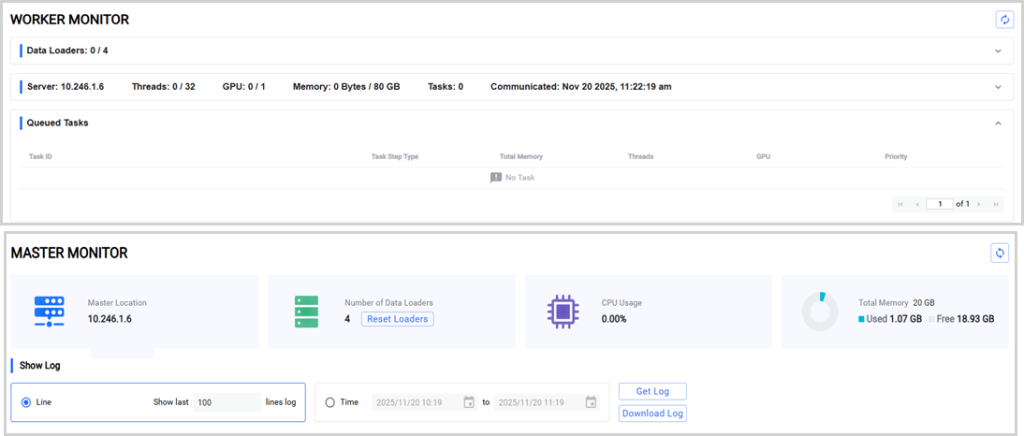
个性化管理系统
通过管理控制功能协调团队工作流,实现分析流、数据库、翻译后修饰(PTM)、定量方法及项目共享的标准化管理。利用工作节点监控器和主节点监控器,轻松实时监控任务进度与交互动态。
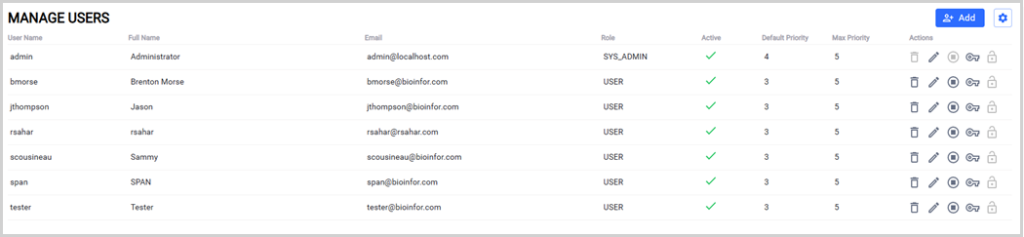
多用户支持
通过用户管理页面,可轻松管理普通用户账户与管理员账户,并支持多用户同时访问 PEAKS Online 服务器。
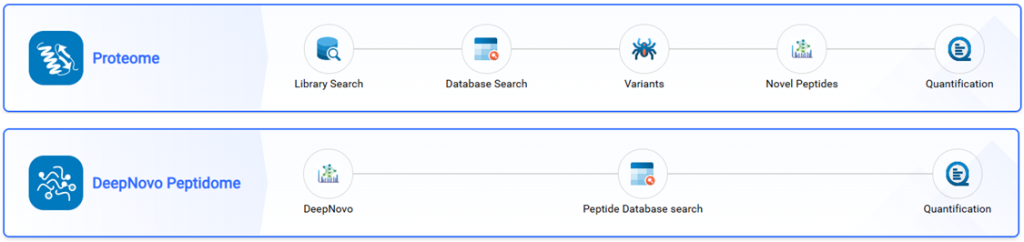
PEAKS DeepNovo 多肽组
DeepNovo 多肽组工作流通过整合全面的基因数据库,弥合蛋白质组学与基因组学之间的研究鸿沟。DDA Peptidome 工作流支持非经典参考序列,能够鉴定标准经典参考数据库中常被遗漏的变异肽段和修饰肽段。DIA Peptidome 工作流现已支持谱库与靶向肽段列表功能,可针对样本中预期存在的目标肽段的精准检索。
DDA Peptidome
DIA Peptidome
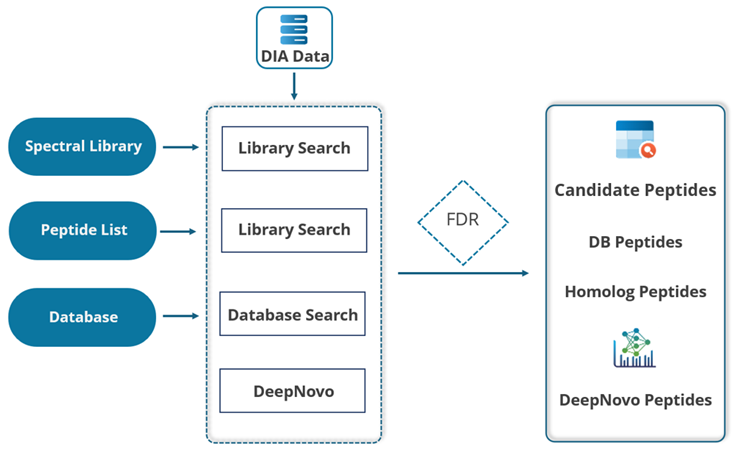
优化 DIA 蛋白质组工作流
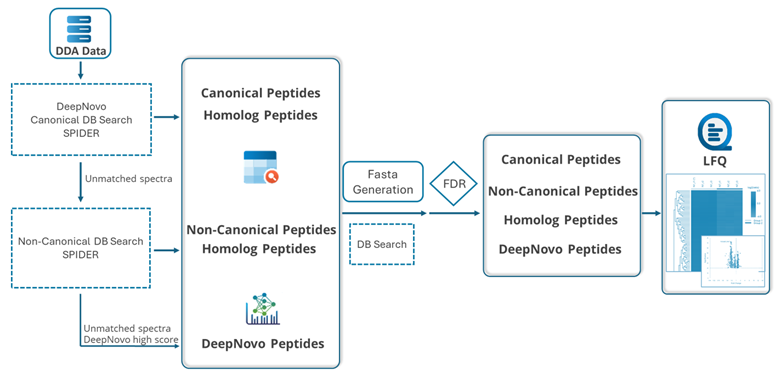
PEAKS 为 DIA 数据分析提供了稳健的解决方案。首先,系统可选择性地对预先构建的谱图库进行匹配搜索。通过估算假阳性率(FDR),将通过筛选的肽段结果保留。未能在FDR阈值范围内匹配到肽段的MS/MS谱图将进入直接数据库搜索阶段,高置信度的数据库匹配结果将被纳入最终分析结果。随后,数据库搜索中未能匹配的谱图将通过从头测序(de novo sequencing)进行分析。通过平均局部置信度评分筛选的肽段将进一步提交至SPIDER算法进行后续分析。
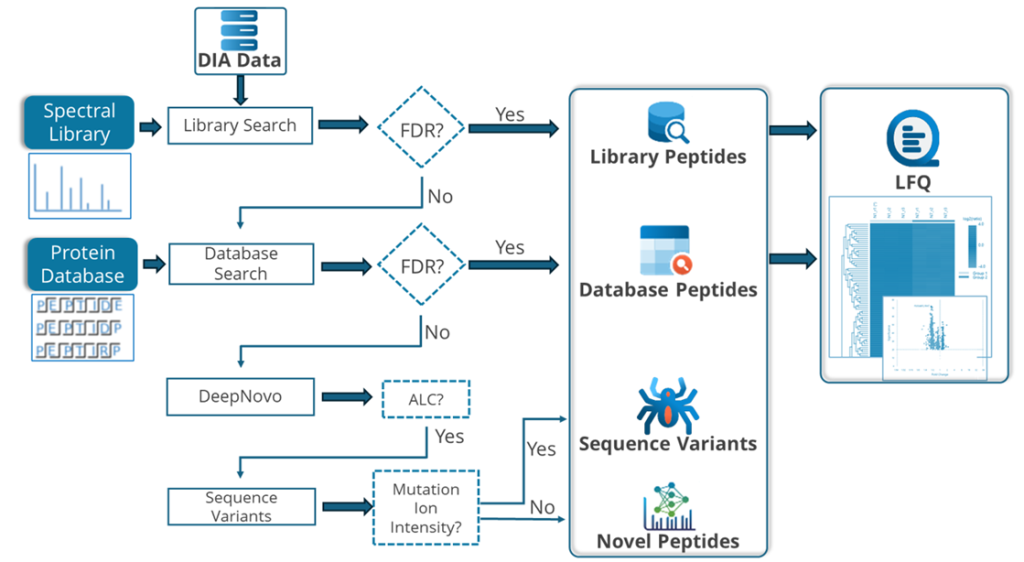
序列变体分析
借助 PEAKS Online,突破传统蛋白质组学的研究边界。通过 SPIDER 算法挖掘序列变异体,依托从头测序(de novo sequencing)发现新型肽段。

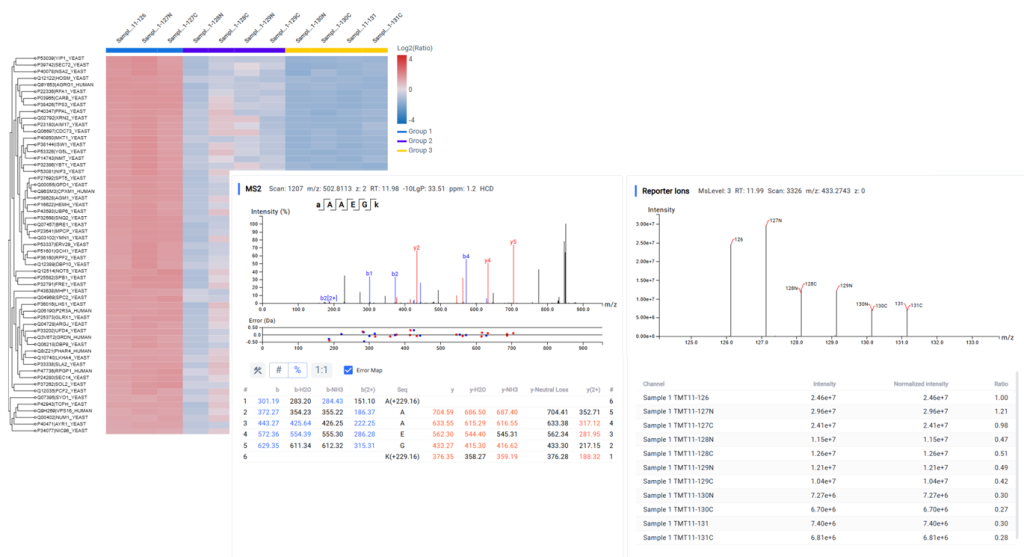
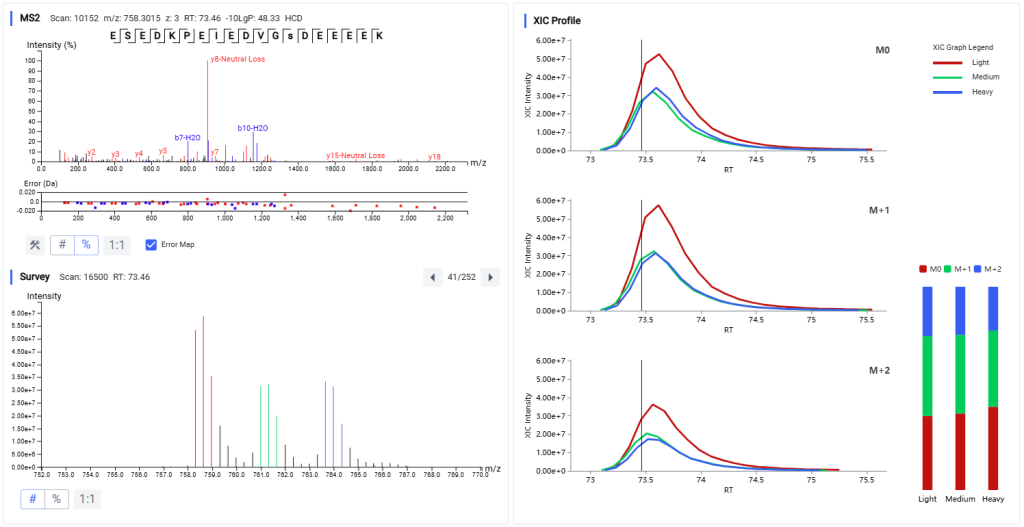
定量分析
PEAKS Q 助力精准发现蛋白质表达变化。用户可针对样本间肽段/蛋白质的表达丰度差异进行深入分析,提供直观的结果(热图、火山图和提取的离子色谱图)来为 DDA 与 DIA 工作流提供精准可靠的定量分析结果。

License Information
- PEAKS Online可以扩展以满足您实验室的需求。PEAKS Online 提供128、256 和 512 个线程,用户人数为 5-8 人。
Configuration
Base requirements
Recommended configuration for 128 thread license:
- CPU Threads: 12 (Master) + 32 per data node + 1 per license thread (172 threads for a single machine 128 thread license).
- Memory: 12 (Master) + 32 per data node + 2.5 per license thread (384gb for a single machine 128 thread license).
Database requirements
128 or 256 thread license: Single PostgreSQL node with 2tb+ SSD storage space
512+ thread license: 2+ PostgreSQL nodes with 2tb+ SSD storage space
GPU Requirements
For running DDA Peptidome or DIA Database Search workflows, it is recommended that your PEAKS Online cluster has access to GPU computation.
The GPU must have NVIDIA CUDA compute capability >= 8.6 with at least 8GB of dedicated memory.
Furthermore, the GPU needs to be updated to CUDA version 12.6 or later. Please find the CUDA Toolkit installer on NVIDIA’s website and install the packaged NVIDIA driver.
Full requirements and installation details can be found in the PEAKS Online 13 Quick User Manual.
References
- Lightbend, Inc. (2011-2019). Akka: Build powerful reactive, concurrent, and distributed applications more easily. https://akka.io/.
- PostgreSQL: The World’s Most Advanced Open Source Relational Database. https://www.postgresql.org/
- Xin, L. Qiao R, Chen X, Tran NH, Pan S, Rabinoviz S, Bian H, He X, Morse B, Shan B, Li M. A streamlined platform for analyzing tera-scale DDA and DIA mass spectrometry data enables highly sensitive immunopeptidomics. Nat. Commun. 13, 3108 (2022). https://doi.org/10.1038/s41467-022-30867-7