PEAKS® AB是一款利用正交酶解方法,通过液相质谱联用产生的数据进行自动化蛋白水平从头测序的软件。通过de Brujin图论的方法将可靠的多肽从头测序片段组装为完整的蛋白序列。
在PEAKS® AB 3.5新版本中,我们对测序技术的精度进一步提高,同时优化了翻译后修饰和结果的呈现。包括:
- 通过保留时间预测优化序列解析
- 完整分子量解卷积算法的优化
- 在序列验证功能中,利用w-ion提供亮氨酸和异亮氨酸的判定建议
- Glycan Profiling 功能中,加入O-linked 糖肽的解析
- 糖肽整合到peptide mapping视图
- 支持timsTOF 数据
- 优化结果展示和报告信息

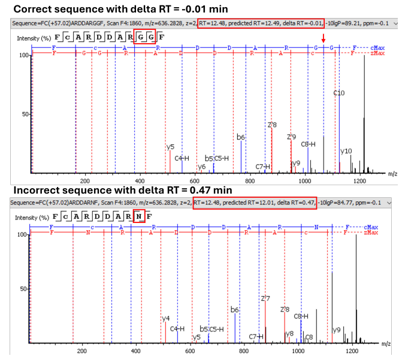
保留时间预测优化序列解析
PEAKS® AB 3.5 中通过引入对保留时间预测,优化序列中等质量的氨基酸残基的区分,能够确保多肽序列的准确测序,进一步确保组装的蛋白序列准确性。在de novo结果中,展示预测保留时间和实测保留时间的差值帮助人工确证。
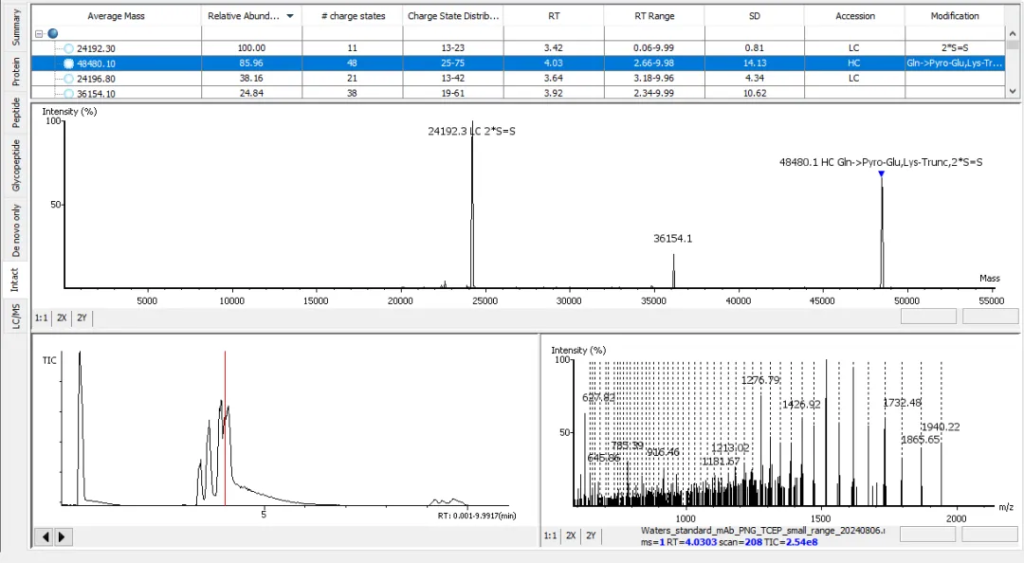
优化的完整分子量解卷积算法
PEAKS® AB 3.5中优化了完整分子量解卷积的算法,得到准确的分子量。同时分子量的测量结果可以用于验证测序组装结果的准确性,并且可以从N端,C端,糖基化修饰等角度来注释分子量的结果。PEAKS® AB软件可以直接整合bottom-up和intact mass 的数据,展示在结果中。
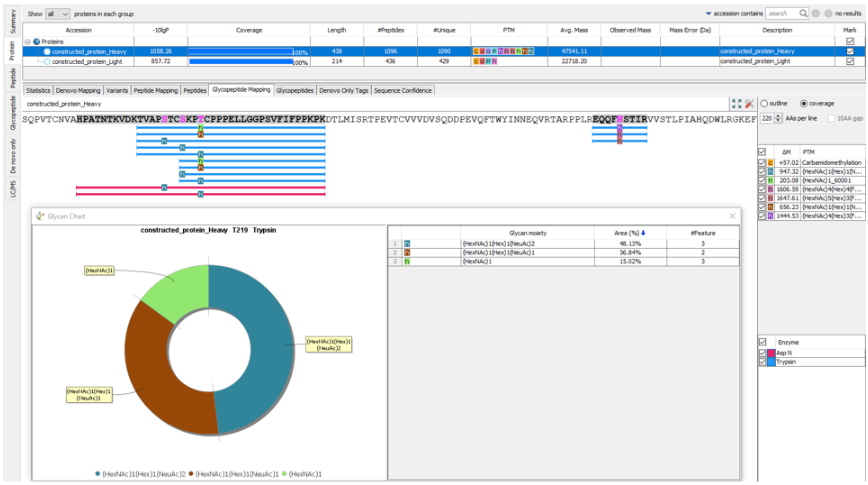
深度糖谱分析
在3.5新版本中,Glycan Profiling功能对抗体重链和/或轻链中鉴定的N-和O-linked位点进行深入的聚糖分析。除了糖肽映射到组装的抗体序列之外,基于不同酶解产物分类的聚糖谱分析显示了在选定的糖基化位点上每个聚糖的组成和相对丰度。并基于与N -linked和O-linked糖库匹配的聚糖片段离子,在每个糖肽谱中提供了聚糖组成和结构的注释信息,和精确的糖基化位点信息。
支持timsTOF 数据
除了Thermo 和SCIEX的数据之外,目前在AB 3.5中,已经支持了timsTOF 的数据。用户可以直接读取Bruker的.d格式原始数据用于蛋白从头测序和序列确证分析。
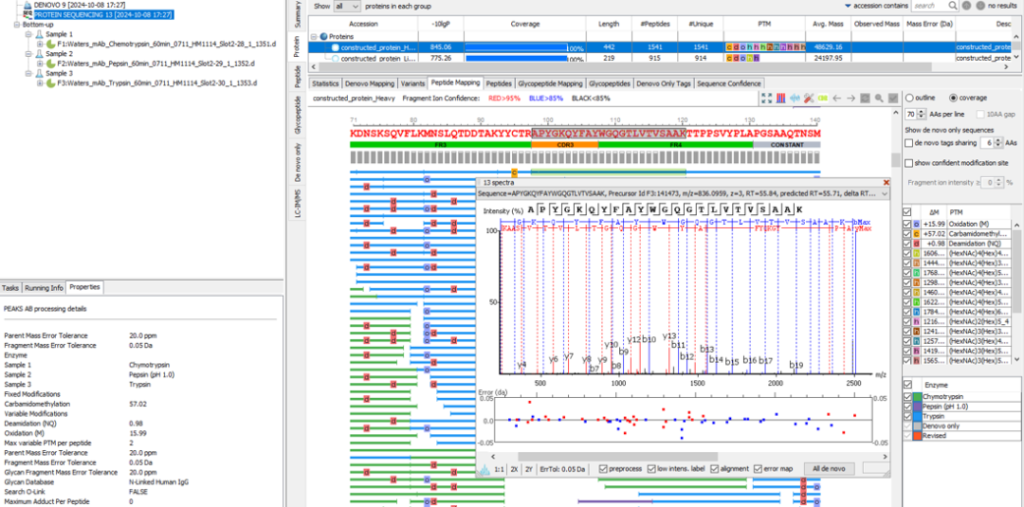
优化的定制化报告功能
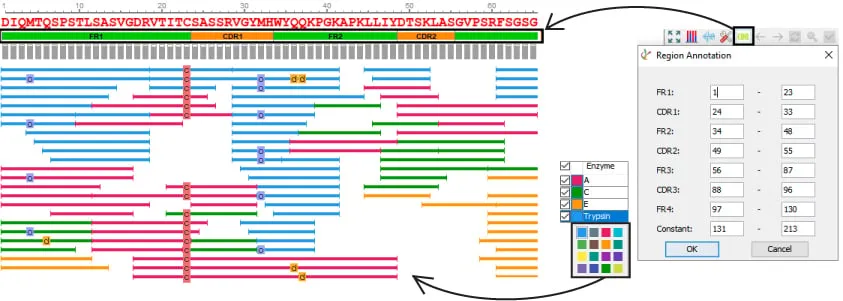
PEAKS® AB 3.5现在为每个PSM应用一个局部置信度(CAA)分数,序列拼接的过程多肽的选择提供更可靠的确证,用户也可以在结果中手动选择代表性peptide。另外,在PTM功能模块中也可以进行抗体序列CDR功能区注释的设置和修改。
参考文献:
Tran, N.H. et al. Complete De Novo Assembly of Monoclonal Antibody Sequences. Scientific Reports. 6:31730. 26/08/2016.

