基于高温蛋白酶与新一代碎裂技术,全面升级抗体从头测序
来自 CinderBio 公司 Steven Yannone 博士团队、与 Albert Heck 博士实验室合作开展的一项最新研究发表于《Cell Systems》。该研究表明:高效高温酸性蛋白酶结合混合碎裂策略,可显著提升从头测序的可靠性。将基于 HTA 的高温单一酶解法与高性能 ZenoTOF EAciD 碎裂技术联用,可获得高信息丰度质谱图,仅通过单次 LC-MS 分析即可实现高置信度的抗体从头测序。
传统胰酶酶解通常产生短肽,对抗体互补决定区(CDR)的覆盖度有限。因此,抗体从头测序通常需要多种蛋白酶、多次质谱分析,流程复杂且成本较高。本研究采用超高温酸性古菌蛋白酶,经一步酶解获得长且重叠的肽段,这些肽段可与PEAKS 从头测序完美适配。
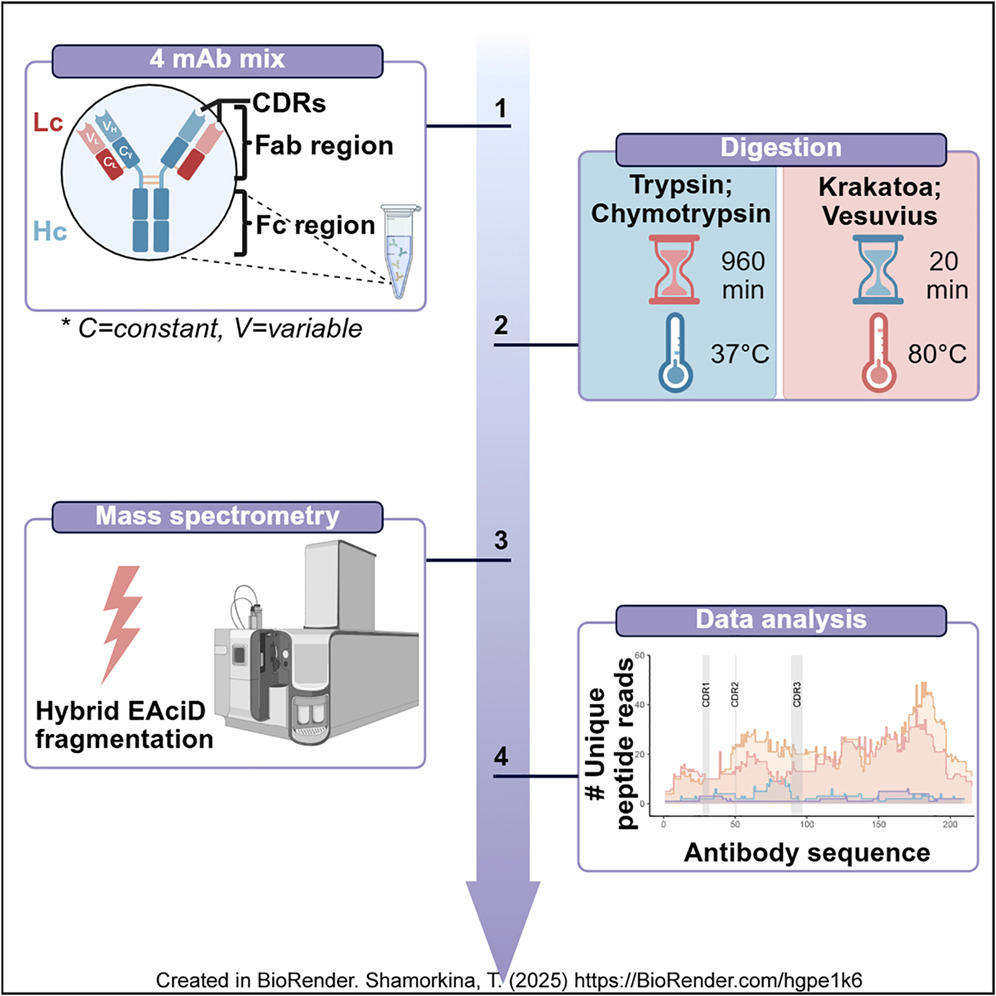
研究证实,PEAKS DeepNovo 肽段测序算法可高效解析 EAciD 碎裂产生的完整碎片离子,输出高置信度肽段序列,在抗体可变区实现单残基水平的可靠判定。依托 PEAKS Studio 获得的高可信肽段序列,可重构包含全部 CDR 的完整抗体序列,相较传统流程,序列置信度更高、错误率更低。
BSI 旗下自动化蛋白与抗体测序工具PEAKS AB已新增HTA 蛋白酶支持,可高效解析新一代碎裂技术下产生的质谱数据、鉴定高可信肽段,助力研究者从质谱数据中挖掘更深层次信息。我们始终坚持以软件技术支撑前沿突破,不断推动抗体测序领域创新。
如您希望了解更多详细信息,欢迎随时联系我们!

